综述|从“看见菌群”到“精准干预”:机器学习推动宿主-微生物组研究迈向“虚拟肠道”


近日,Science China Life Sciences(《中国科学:生命科学》英文版)在线发表湖南农业大学谭碧娥教授、王婧教授与中国科学院亚热带农业生态研究所印遇龙院士团队撰写综述文章“Integrating host-microbiome multi-omics with machine learning: methods, benchmarks, and translational applications”,系统总结了宿主-微生物组多组学整合与机器学习分析的关键方法、评估框架及转化应用前景,为推动宿主-微生物互作研究由相关性描述迈向机制解析和精准干预提供了重要参考。

宿主—微生物互作在代谢调控、免疫稳态、肠道屏障维护及疾病发生发展中发挥重要作用。随着基因组学、转录组学、蛋白质组学、代谢组学以及单细胞和空间组学技术的发展,研究者已能够更系统地解析宿主与微生物之间的复杂关系。然而,多组学数据具有高维、异质、稀疏和批次效应强等特点,给整合分析与稳健建模带来了较大挑战。
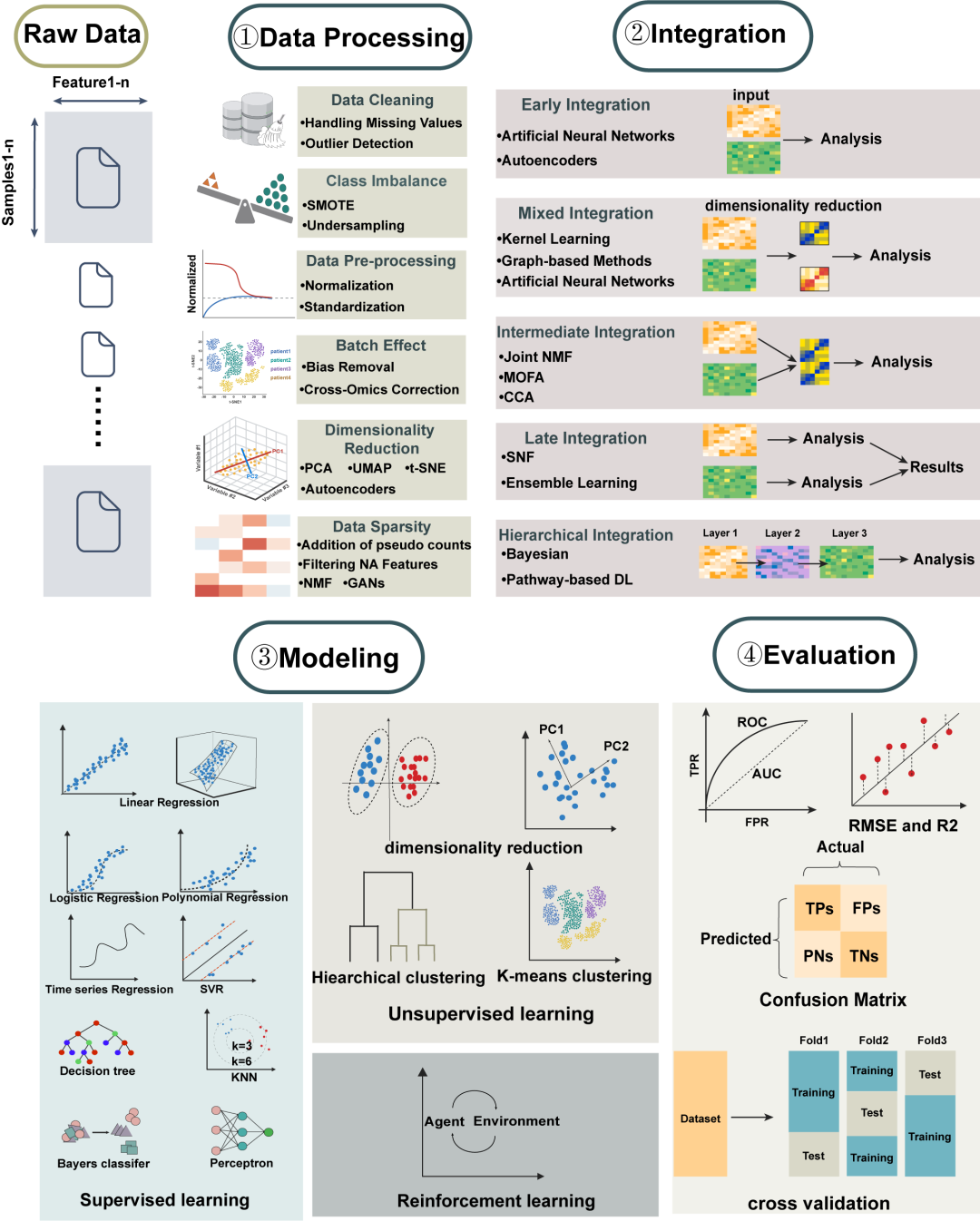
图1 宿主—微生物多组学整合与机器学习分析框架
文章重点梳理了多组学整合的主要策略及随机森林、支持向量机、深度学习、图神经网络和大语言模型等方法在宿主—微生物研究中的应用,指出机器学习不仅可提升疾病预测和分型能力,也有助于识别关键菌群、宿主因子及潜在调控通路。同时,作者强调,应更加关注模型的可解释性、跨队列泛化能力以及实验验证闭环,以推动该领域真正实现临床和产业转化。
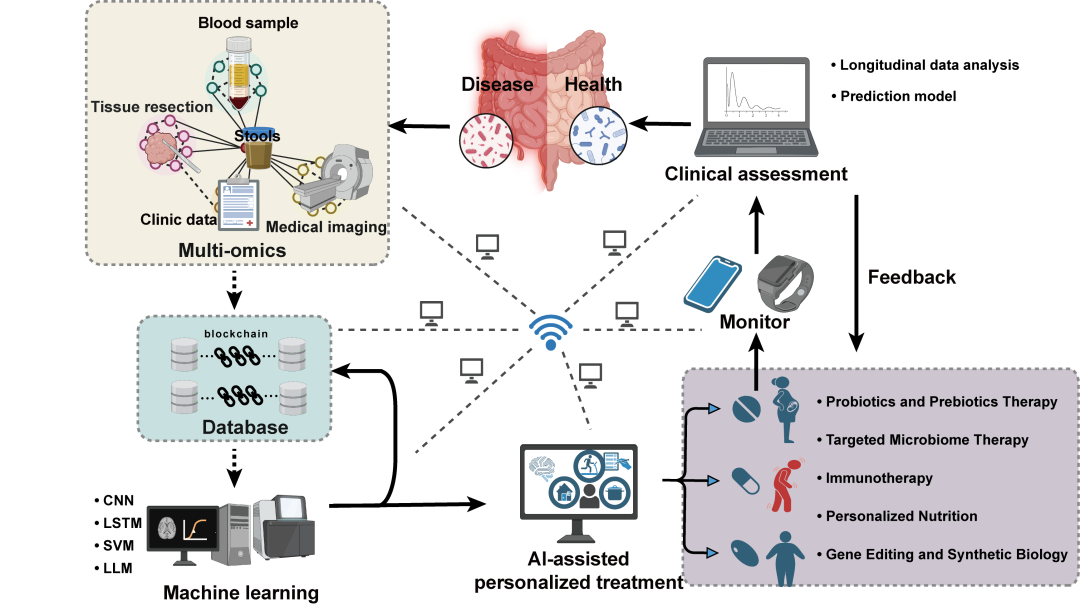
图2 面向精准干预的AI驱动宿主—微生物多组学整合框架
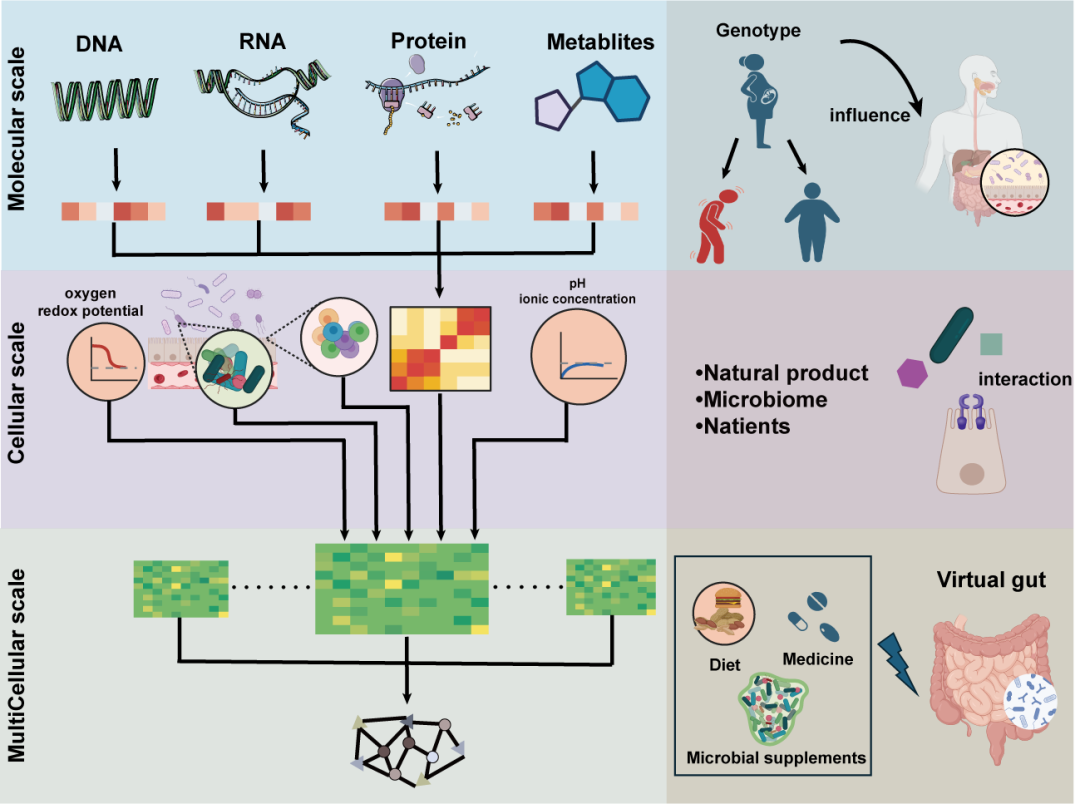
图3 基于AI的虚拟肠道的构建
在应用层面,作者进一步展望了宿主—微生物研究在精准营养、疾病分层、治疗反应预测、肠道虚拟建模以及合成微生物群设计等方向的广阔前景。文章提出,随着公共数据库建设、联邦学习、隐私保护计算和标准化评估体系的不断完善,未来有望构建融合宿主组学、微生物组学、临床表型和动态监测数据的“虚拟肠道”平台,并结合机器学习实现个体化干预方案设计。同时,机器学习与合成生物学的结合也将推动功能菌群设计、工程菌开发和精准微生态治疗向更高水平发展。整体而言,该综述从方法学、应用场景和未来趋势三个层面,系统描绘了宿主-微生物多组学与人工智能融合发展的技术路线图,为医学、农业及环境领域相关研究提供了重要参考。
湖南农业大学沈海波博士、张龙林博士、马晓康副教授为共同第一作者,湖南农业大学谭碧娥教授、王婧教授与中国科学院亚热带农业生态研究所印遇龙研究员为共同通讯作者。
[点击下方链接或阅读原文]▼
https://doi.org/10.1007/s11427-025-3163-6


